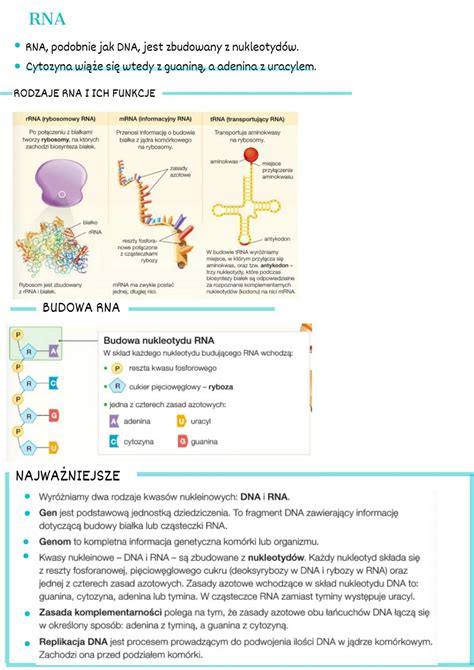
Genetyka, jako dziedzina nauki, nieustannie poszerza nasze rozumienie życia na poziomie molekularnym. Kluczowym etapem w wielu badaniach genetycznych, od podstawowych analiz laboratoryjnych po zaawansowaną diagnostykę medyczną, jest izolacja DNA. Proces ten polega na oczyszczaniu materiału genetycznego z innych składników chemicznych i biologicznych obecnych w próbce. Izolacja DNA jest fundamentem, na którym opiera się wiele odkryć i innowacji, umożliwiając analizę genomu, zrozumienie przyczyn chorób oraz rozwój personalizowanych terapii. Od pierwszego wyizolowania DNA w roku 1869 przez Friedricha Mieschera, metody jego pozyskiwania ewoluowały, stając się coraz bardziej precyzyjne, szybkie i dostępne. Dziś proces ten obejmuje zarówno techniki manualne, wymagające precyzji i doświadczenia, jak i zaawansowane systemy automatyczne, które rewolucjonizują pracę laboratoriów.
Fundamenty Izolacji DNA: Zniszczenie Komórek i Oczyszczenie
Podstawowym celem izolacji DNA jest wydobycie tej cennej cząsteczki z jej naturalnego środowiska - komórki - i uwolnienie jej od towarzyszących jej elementów, takich jak białka, lipidy, czy inne kwasy nukleinowe. Cały proces można podzielić na kilka kluczowych etapów, które są obecne zarówno w metodach manualnych, jak i automatycznych, choć realizowane w różny sposób i z różnym stopniem zaawansowania technologicznego.
Pierwszym krokiem jest zniszczenie komórek, czyli tak zwana liza. Ma to na celu uwolnienie DNA z wnętrza komórki, a w przypadku organizmów eukariotycznych - również z jądra komórkowego. Metody fizyczne, takie jak homogenizacja, mogą być stosowane do rozdrabniania tkanek, podczas gdy metody chemiczne wykorzystują detergenty i enzymy do rozrywania błon komórkowych i ścian komórkowych. Na przykład, organizmy z grubą ścianą komórkową, takie jak niektóre bakterie, wymagają bardziej intensywnego rozpadu komórek, co może wpływać na stopień fragmentacji izolowanego DNA. Po zniszczeniu komórek, DNA znajduje się w roztworze, ale wciąż jest zmieszane z licznymi innymi związkami.
Kolejnym, niezwykle ważnym etapem jest oczyszczenie DNA z tych zbędnych składników. Należą do nich przede wszystkim białka, które mogą zakłócać dalsze analizy enzymatyczne, a także sole i detergenty użyte we wcześniejszych krokach. Usunięcie białek jest kluczowe, ponieważ wiele enzymów wykorzystywanych w biologii molekularnej jest wrażliwych na ich obecność.
Ostatnim etapem jest zazwyczaj precypitacja DNA, czyli wytrącenie go z roztworu. Odbywa się to poprzez dodanie zimnego alkoholu, zazwyczaj etanolu lub izopropanolu. Alkohol zmniejsza rozpuszczalność DNA w wodzie, powodując jego agregację i wytrącenie. Po dodaniu alkoholu i odczekaniu odpowiedniego czasu, cząsteczki DNA osadzają się na dnie probówki, często po odwirowaniu, tworząc widoczny osad. Ten osad można następnie zebrać i rozpuścić w odpowiednim buforze, przygotowując go do dalszych zastosowań.
Klasyczne Metody Manualne: Precyzja i Wymagający Protokół
Przez lata rozwinięto szereg manualnych metod izolacji DNA, które nadal stanowią punkt odniesienia i są stosowane w wielu laboratoriach, zwłaszcza tam, gdzie wymagana jest elastyczność i możliwość optymalizacji protokołu dla specyficznych typów próbek.
Jedną z historycznie znaczących i wciąż użytecznych, choć coraz rzadziej stosowanych w rutynowej pracy ze względu na czasochłonność i toksyczność odczynników, jest ekstrakcja fenol-chloroformowa. W tej metodzie, po lizie komórek, do próbki dodawana jest mieszanina fenolu i chloroformu. Fenol denaturuje białka, powodując ich koagulację. Po odwirowaniu próbki, tworzą się trzy fazy: fazę wodną, zawierającą kwasy nukleinowe (DNA i RNA), fazę organiczną, zawierającą białka i lipidy, oraz fazę pośrednią. Kwasy nukleinowe są następnie pobierane z fazy wodnej. Chociaż metoda ta pozwala na uzyskanie czystego i zazwyczaj niezdegradowanego DNA, wymaga ostrożności ze względu na toksyczność fenolu i chloroformu oraz generuje odpady laboratoryjne, które wymagają specjalnego traktowania. Jest ona nadal stosowana do izolacji DNA z "bloczków parafinowych", gdzie inne metody mogą być mniej efektywne.
Inną popularną metodą manualną, często wykorzystywaną w diagnostyce i badaniach, jest oczyszczanie na mikrokolumnach wirówkowych. Metoda ta opiera się na zjawisku adsorpcji kwasów nukleinowych na specjalnym materiale - zazwyczaj są to ziarna krzemionki (silica), ale mogą być również inne adsorbenty. Po lizie komórek i etapie usuwania białek, próbka jest przepuszczana przez kolumnę zawierającą adsorbent. W odpowiednich warunkach buforowych (zazwyczaj w obecności chaotropów, takich jak guanidyna), DNA wiąże się do powierzchni krzemionki. Następnie, przez serię płukań z użyciem różnych roztworów buforowych, usuwane są wszelkie zanieczyszczenia. Na końcu, DNA jest wymywane z kolumny przy użyciu buforu o niskiej sile jonowej lub wody. Ta metoda jest szybsza i bezpieczniejsza niż ekstrakcja fenol-chloroformowa, a dzięki gotowym zestawom odczynników jest łatwa do wdrożenia w większości laboratoriów. Pozwala ona na uzyskanie DNA o wysokiej czystości, odpowiedniego do dalszych analiz, takich jak PCR czy sekwencjonowanie.
Potwierdzanie Obecności i Jakości DNA: Testy i Analizy
Po przeprowadzeniu procesu izolacji, kluczowe jest potwierdzenie obecności DNA oraz ocena jego czystości i integralności. Istnieje kilka standardowych metod, które pozwalają na weryfikację jakości otrzymanego preparatu.
Jedną z prostych metod chemicznych potwierdzających obecność DNA jest reakcja z difenyloaminą. Procedura ta polega na chemicznej hydrolizie DNA podczas ogrzewania do temperatury powyżej 95°C z dodatkiem kwasu. W wyniku tego procesu uwalniana jest między innymi deoksyryboza - cukier charakterystyczny dla DNA, a nieobecny w RNA. Deoksyryboza następnie reaguje z difenyloaminą, tworząc związek o intensywnie niebieskiej barwie - aldehyd hydroksylewulinowy. Intensywność niebieskiego zabarwienia jest proporcjonalna do ilości obecnego DNA.
Bardziej precyzyjną metodą oceny czystości preparatu DNA jest pomiar absorbancji światła przy określonych długościach fal przy użyciu spektrofotometru. DNA silnie absorbuje promieniowanie ultrafioletowe o długości fali 260 nm. Białka z kolei, ze względu na obecność w ich strukturze aminokwasów aromatycznych, absorbują promieniowanie o długości fali 280 nm. Czysta próbka DNA powinna wykazywać stosunek absorbancji 260/280 na poziomie około 1.8. Znacznie niższy stosunek może wskazywać na obecność zanieczyszczeń białkowych, podczas gdy wyższy stosunek może sugerować obecność RNA. Analiza stosunku absorbancji 260/230 nm pozwala z kolei ocenić obecność innych zanieczyszczeń, takich jak sole czy rozpuszczalniki organiczne, dla których optymalny stosunek wynosi około 2.0-2.2.
Weryfikacja integralności DNA, czyli sprawdzenie, czy cząsteczki nie uległy znacznemu zdegradowaniu, jest możliwa poprzez trawienie enzymami restrykcyjnymi i analizę elektroforetyczną w żelu agarozowym. Enzymy restrykcyjne przecinają DNA w specyficznych miejscach. Jeśli DNA jest w całości, enzymy te wytworzą określoną populację fragmentów o określonych długościach. Po przeprowadzeniu reakcji trawienia i dodaniu barwnika fluorescencyjnego (np. bromku etydyny lub nowocześniejszych i bezpieczniejszych barwników), produkty trawienia są rozdzielane w żelu agarozowym pod wpływem pola elektrycznego. W zależności od wielkości fragmentów, migrują one z różną prędkością, tworząc charakterystyczny wzór prążków. Obecność szerokiego, rozmazanego pasma zamiast wyraźnych prążków może świadczyć o degradacji DNA.
Automatyzacja Procesów: Szybkość, Wydajność i Powtarzalność
Dynamiczny rozwój nauk biologicznych i medycznych, w tym medycyny spersonalizowanej, sekwencjonowania nowej generacji (NGS) czy PCR w czasie rzeczywistym (qPCR), wymusił potrzebę doskonalenia i automatyzacji metod izolacji kwasów nukleinowych. Nowe metody, takie jak płynna biopsja (liquid biopsy), która pozwala na analizę materiału genetycznego krążącego we krwi, rewolucjonizują diagnostykę, ale jednocześnie stawiają wysokie wymagania co do jakości i czystości izolowanego DNA i RNA.
Systemy automatyczne oferują znaczące korzyści w porównaniu do metod manualnych, takie jak zwiększona przepustowość, lepsza powtarzalność wyników, skrócenie czasu potrzebnego na analizę oraz minimalizacja ryzyka błędu ludzkiego i kontaminacji.
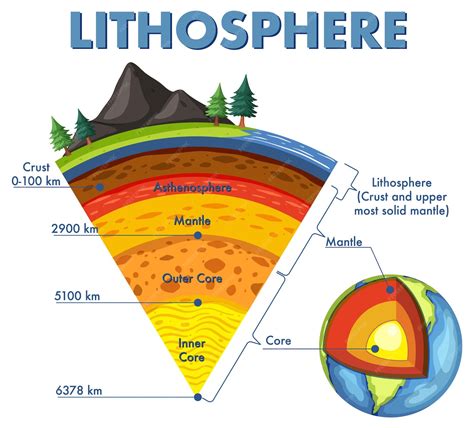
Jednym z rozwiązań na rynku jest system MagCore® EDA firmy RBC Bioscience. Pozwala on na automatyczną izolację kwasów nukleinowych z szerokiej gamy materiałów, w tym krwi, tkanek, komórek, bakterii, wirusów i tkanek roślinnych. System ten wykorzystuje technologię kulek magnetycznych. W procesie tym, na specjalnie przygotowanych magnetycznych kuleczkach, które silnie wiążą DNA lub RNA, osadzają się cząsteczki kwasów nukleinowych. Następnie, za pomocą pola magnetycznego, kulki z przyłączonym materiałem genetycznym są przenoszone pomiędzy kolejnymi roztworami - buforem lizującym, buforami płuczącymi i buforem eluującym. Taka separacja cieczy od fazy stałej bez potrzeby fizycznego pipetowania znacznie zmniejsza ryzyko kontaminacji i błędów. System MagCore® EDA posiada wysoką przepustowość, umożliwiając izolację do 24 próbek w jednym przebiegu, co zajmuje od 30 do 120 minut, w zależności od zastosowanego protokołu. Możliwe jest także przetwarzanie pojedynczych próbek, co eliminuje straty odczynników przy mniejszej liczbie badań. Instrument wyposażony jest w lampę UV, która pomaga minimalizować ryzyko kontaminacji próbek i zapewnia bezpieczeństwo użytkownika. Możliwość podłączenia systemu do sieci informatycznej (LIS) oraz wbudowany czytnik kodów kreskowych usprawniają identyfikację próbek i zarządzanie danymi. System MagCore EDA może również automatycznie przygotować reakcje PCR.

Innym przykładem zaawansowanego systemu automatyzującego izolację kwasów nukleinowych jest seria Maxwell® firmy Promega. Urządzenia te, obecne na rynku od ponad dekady, cieszą się uznaniem naukowców na całym świecie. Szczególnie istotna jest technologia Maxwell® CSC (Clinical Sample Concentrator), opracowana z myślą o wymogach diagnostyki klinicznej. Proces produkcji tych urządzeń i zestawów odczynników odbywa się zgodnie z zasadami Dobrej Praktyki Wytwarzania (cGMP), co umożliwiło uzyskanie europejskiego certyfikatu CE-IVD.
Działanie systemu Maxwell® opiera się również na wykorzystaniu cząsteczek paramagnetycznych, które selektywnie wiążą kwasy nukleinowe. Proces izolacji jest prosty i zautomatyzowany. Po dodaniu próbki do specjalnego kartridża, wszystkie kolejne kroki są wykonywane przez urządzenie. Kwasy nukleinowe są transportowane pomiędzy buforami płuczącymi dzięki przyciąganiu magnetycznemu, co eliminuje potrzebę wielokrotnego pipetowania i znacząco redukuje ryzyko kontaminacji w porównaniu do metod hydraulicznych. Wydajność i jakość uzyskanego produktu są bardzo wysokie, co potwierdzono w licznych badaniach. System Maxwell® oferuje zestawy do izolacji DNA i RNA z różnorodnych materiałów, takich jak krew, osocze, ślina, tkanki stałe (świeże, utrwalone w formalinie i zatopione w parafinie - FFPE), a także specjalistyczne produkty do oczyszczania wolnego pozakomórkowego DNA (ccfDNA), miRNA czy genomu wirusowego.

Pomimo zaawansowania technologicznego, urządzenia takie jak Maxwell® charakteryzują się kompaktowymi rozmiarami, nie zajmując na stole laboratoryjnym więcej miejsca niż przeciętny laptop. Utrzymanie ich w czystości ułatwia wbudowana lampa UV. Urządzenie umożliwia jednoczesne oczyszczenie do 16 próbek, ale równie efektywnie może przetworzyć pojedynczą próbkę, bez marnowania odczynników. Przejrzyste oprogramowanie z preinstalowanymi protokołami i intuicyjny interfejs użytkownika, sterowany ekranem dotykowym, sprawiają, że obsługa jest prosta i szybka. Wbudowany czytnik kodów kreskowych ułatwia identyfikację próbek i zapis danych.
Nowe Wyzwania i Przyszłość Izolacji DNA
Rozwój takich technik jak sekwencjonowanie nowej generacji (NGS) czy coraz powszechniejsze wykorzystanie materiału genetycznego w diagnostyce klinicznej i medycynie spersonalizowanej stawia przed metodami izolacji DNA nowe wyzwania. Przykładowo, analiza szczątków ludzkich, nawet tych bardzo starych i częściowo zdegradowanych, wymaga zastosowania specjalistycznych, wydajnych i zautomatyzowanych protokołów. Eksperci wykazali, że zastosowanie nowych protokołów z wykorzystaniem urządzeń takich jak EZ2 Connect pozwala na efektywną i zautomatyzowaną ekstrakcję DNA ze starego materiału kostnego, pochodzącego z różnych środowisk, także tych sprzyjających degradacji DNA. Usprawnia to proces identyfikacji genetycznej szczątków ludzkich i pomaga innym ekspertom we wdrożeniu podobnych metod.
W kontekście diagnostyki dziedzicznych predyspozycji do nowotworów, kluczowe jest wykrywanie mutacji konstytucyjnych, obecnych we wszystkich komórkach pacjenta. Materiał do izolacji DNA stanowią na ogół łatwo dostępne komórki, takie jak leukocyty z krwi obwodowej. Materiał ten można pobrać bezpośrednio przed izolacją, ale dobre wyniki uzyskuje się również po kilkudniowym przechowywaniu krwi w temperaturze pokojowej lub nawet przez wiele lat w temperaturze poniżej zera. Izolacja DNA z tkanek utrwalonych w formalinie i zatopionych w bloczkach parafinowych (FFPE) jest możliwa, lecz uzyskanie jednoznacznych wyników z takiego materiału bywa trudne lub wręcz niemożliwe z powodu potencjalnej degradacji DNA.
MagnifiQ™. Automatyczna izolacja kwasów nukleinowych
Postęp w biologii molekularnej przejawia się także w rozwoju metod wykrywania zmian genetycznych. Poza sekwencjonowaniem, które jest najbardziej czułą techniką umożliwiającą pełną charakterystykę zmian, stosuje się techniki takie jak DHPLC (Denaturing High-Performance Liquid Chromatography), która wykorzystuje wysoką rozdzielczość kolumn chromatograficznych do wykrywania heterodupleksów DNA w warunkach subdenaturacyjnych. Metoda ta łączy zalety dotychczas stosowanych technik. Pojawienie się wielofunkcyjnych robotów laboratoryjnych umożliwiło również całkowitą automatyzację procesów takich jak normalizacja stężeń rozcieńczanych próbek czy przygotowanie reakcji PCR. Równoczesny rozwój oprogramowania i komputeryzacja pozwoliły na automatyczne zarządzanie dużymi seriami próbek, łącznie z transferem wyników, co jest nieocenione w laboratoriach o wysokiej przepustowości.
Warto również wspomnieć o izolacji RNA, która wymaga jeszcze większej staranności ze względu na wszechobecność termostabilnych RNaz. Powszechnie stosowaną metodą jest procedura oparta na lizie komórek w roztworze rodanku guanidyny (inhibitora RNaz) i ekstrakcji mieszaniną fenolu i chloroformu. Po izolacji RNA można przepisać na cDNA (komplementarne DNA) za pomocą odwrotnej transkryptazy, a następnie namnożyć przy pomocy reakcji PCR. RNA nie zawiera intronów, co często ułatwia powielenie kodującej części genu.
Przyszłość izolacji DNA i RNA leży w dalszej miniaturyzacji, zwiększeniu szybkości i dokładności, a także w integracji z innymi technologiami analitycznymi. Automatyzacja procesów, rozwój nowych materiałów adsorbentowych i innowacyjnych buforów będą nadal kształtować krajobraz biologii molekularnej, umożliwiając coraz głębsze poznanie genomu i jego implikacji dla zdrowia i chorób człowieka.
Tagi: #genetyka #izolacja #dna #reczna #i #automatyczn